Tests Post-Hoc
Cours 4
Université de la Polynésie française
UE 6.7 Biostatistiques 2
Résumé du cours précédent
Qu’est-ce qu’un modèle statistique ?
“Description probabiliste de la génération des données par des processus sous-jacents”
Probabiliste : Distribution normale, définie par la moyenne (\(\mu\)) et l’écart-type (\(\sigma\)) :
\(\mathrm{y}_i \sim \mathrm{Normal(\mu}_i,~\mathrm{\sigma)}\)
Processus sous-jacents : Variables explicatives, décrivant la valeur attendue \(\mu\)
Résumé du cours précédent
Résumé du cours précédent
Résumé du cours précédent
Résumé du cours précédent
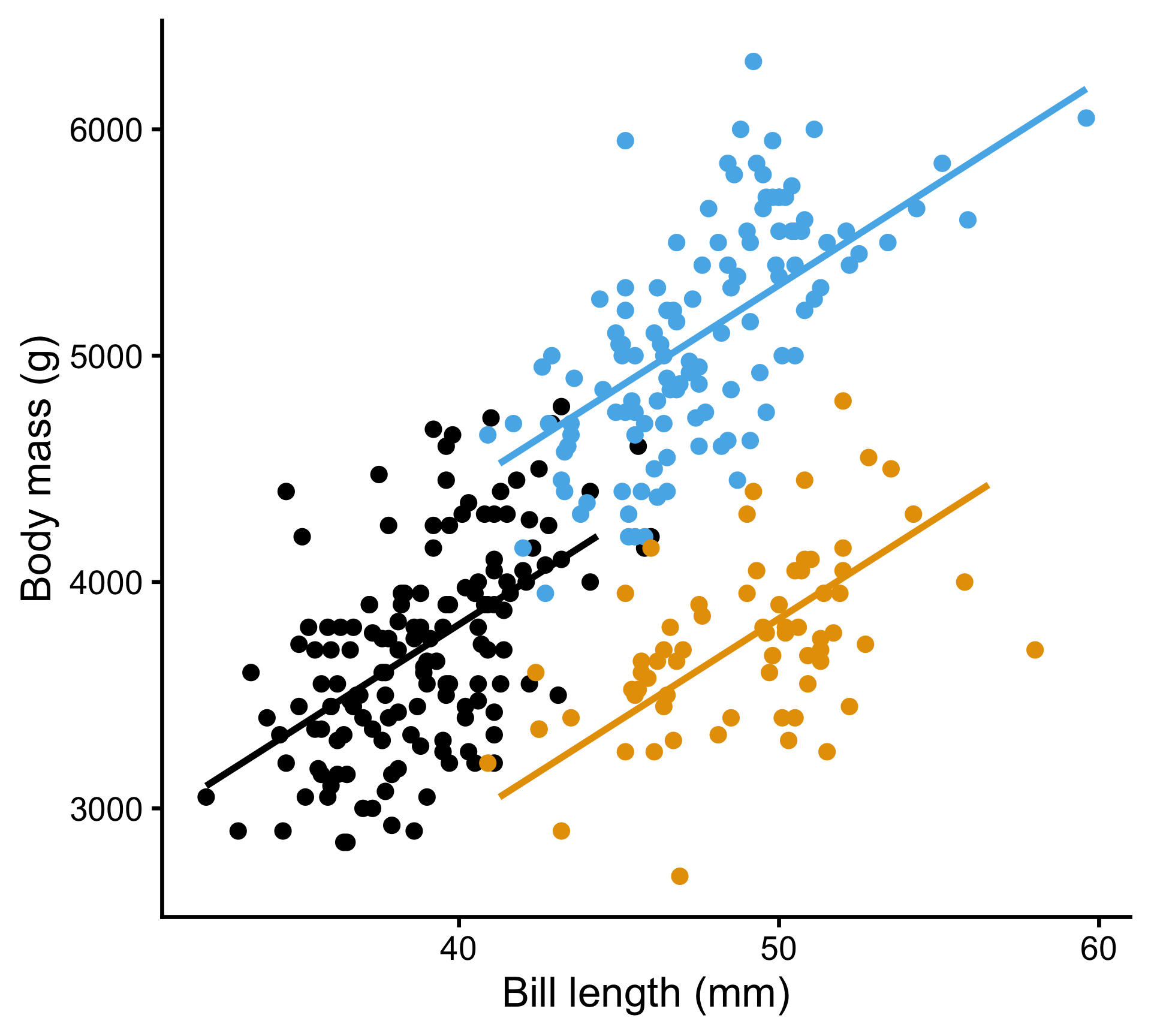
La masse dépend de la taille des manchots et de l’espèce (même pente)
\[ \begin{align} \mathrm{Weight}_i &\sim \mathrm{Normal}(\mu_i,~\sigma) \\ \mu_i &= a_{\text{species}[i]} + b \cdot \mathrm{billlength}_i \end{align} \]
ANCOVA
Résumé du cours précédent
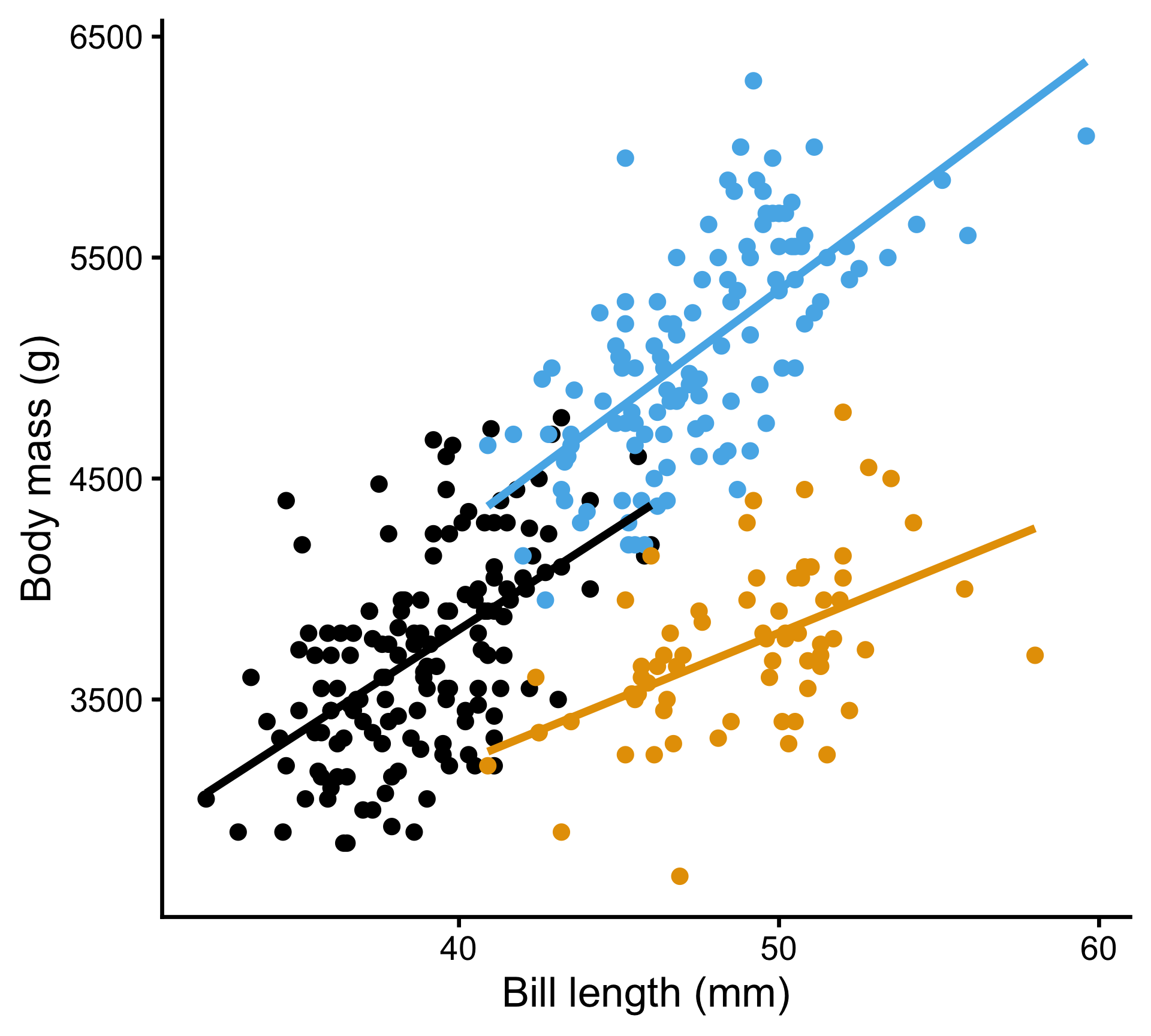
La masse dépend de la taille des manchots et de l’espèce (pentes différentes par espèce)
\[ \begin{align} \mathrm{Weight}_i &\sim \mathrm{Normal}(\mu_i,~\sigma) \\ \mu_i &= a_{\text{species}[i]} + b_{\text{species}[i]} \cdot \mathrm{billlength}_i \end{align} \]
ANCOVA
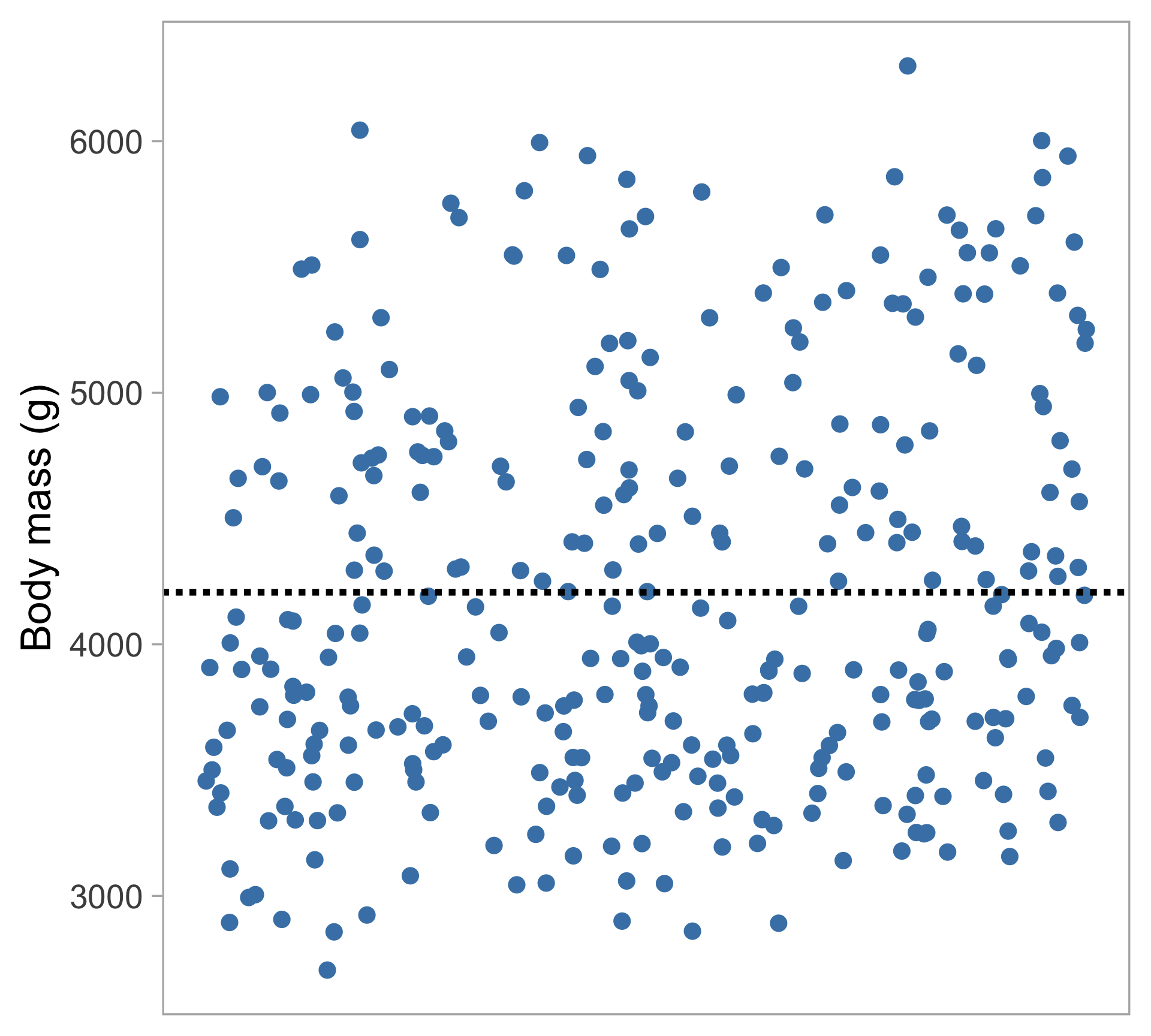
Le problème avec l’ANOVA
Le problème avec l’ANOVA
Analysis of Variance Table
Response: body_mass_g
Df Sum Sq Mean Sq F value Pr(>F)
species 2 145190219 72595110 341.89 < 2.2e-16 ***
Residuals 330 70069447 212332
---
Signif. codes: 0 '***' 0.001 '**' 0.01 '*' 0.05 '.' 0.1 ' ' 1L’ANOVA nous dit : « Il y a une différence entre les espèces »
Mais laquelle des espèces diffère des autres ?
Comparaisons multiples
Pour 3 espèces, nous avons 3 comparaisons possibles :
- Adelie vs. Chinstrap
- Adelie vs. Gentoo
- Chinstrap vs. Gentoo
Pourquoi ne pas simplement faire 3 modèles ?
Inflation de l’erreur alpha
- Chaque test a un risque d’erreur de 5% (α = 0,05)
- Probabilité de ne pas faire d’erreur dans 1 test : 0,95
- Probabilité de ne pas faire d’erreur dans 3 tests : \(0.95 \times 0.95 \times 0.95 = 0.857\)
- Probabilité de faire au moins 1 erreur : \(1 - 0.857 = 0.143 = 14.3\%\)
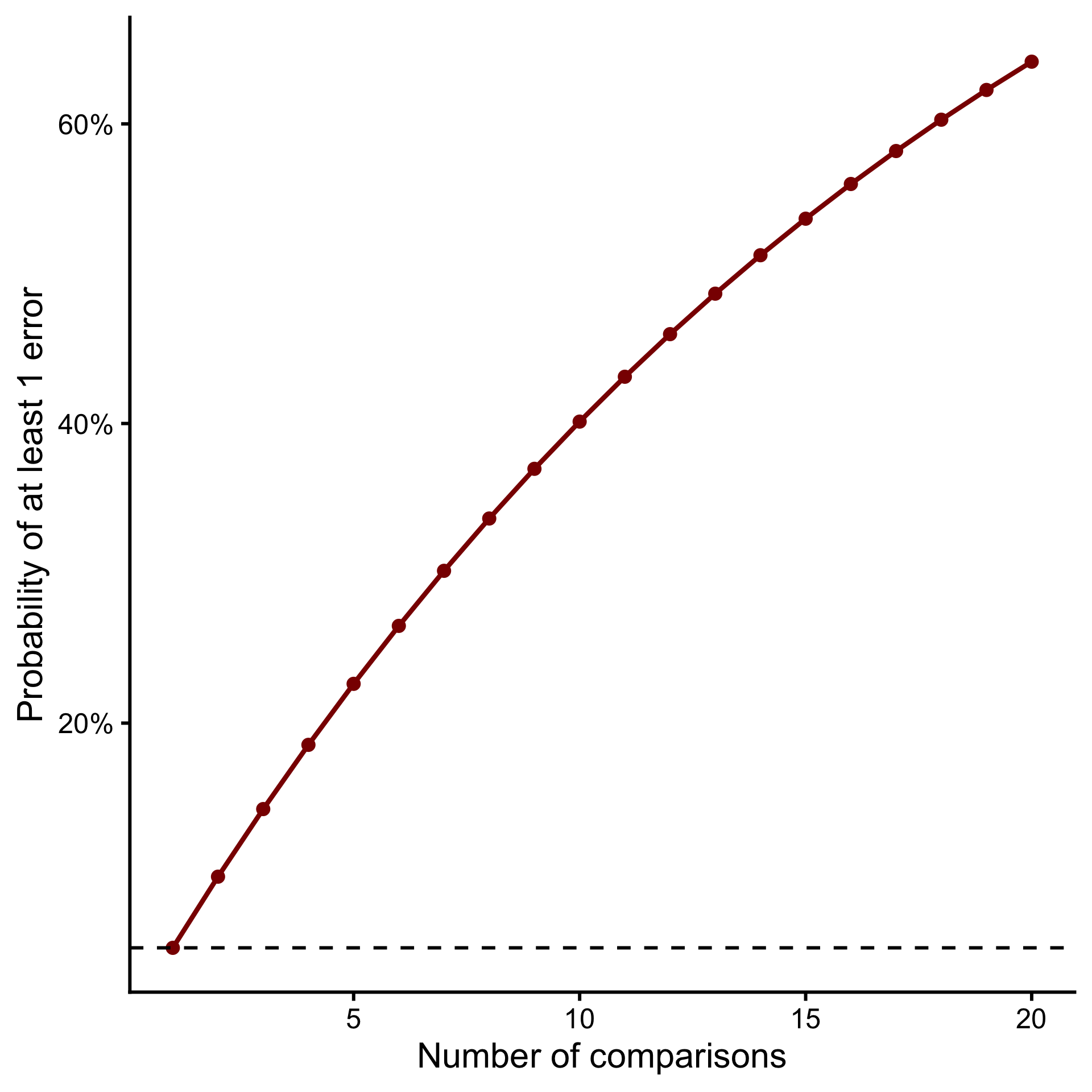
Family-wise error rate (FWER)
FWER : La probabilité de faire au moins une erreur de type I dans un ensemble de tests
| Nombre de groupes | Nombre de comparaisons | FWER (sans correction) |
|---|---|---|
| 2 | 1 | 5,0% |
| 3 | 3 | 14,3% |
| 4 | 6 | 26,5% |
| 5 | 10 | 40,1% |
| 10 | 45 | 90,0% |
Nous devons ajuster nos valeurs p pour contrôler le FWER
Ajustement des valeurs p
| Méthode | Description | Quand l’utiliser |
|---|---|---|
| Bonferroni | Divise α par le nombre de tests | Tests simples, peu de tests |
| Holm-Bonferroni | Bonferroni séquentiel (moins strict) | Alternative à Bonferroni |
| Benjamini-Hochberg | Contrôle le taux de fausses découvertes | Beaucoup de tests |
| Tukey HSD | Tient compte de toutes les comparaisons | Comparaisons multiples |
Les tests de Tukey sont souvent utilisés pour les tests post-hoc
Tests post-hoc en R
m_spec <- lm(body_mass_g ~ species, data = penguins)
library(modelbased)
estimate_contrasts(m_spec, p_adjust = "tukey")Marginal Contrasts Analysis
Level1 | Level2 | Difference | SE | 95% CI | t(330) | p
---------------------------------------------------------------------------------
Chinstrap | Adelie | 26.92 | 67.65 | [-106.16, 160.01] | 0.40 | 0.916
Gentoo | Adelie | 1386.27 | 56.91 | [1274.32, 1498.22] | 24.36 | < .001
Gentoo | Chinstrap | 1359.35 | 70.05 | [1221.55, 1497.15] | 19.41 | < .001
Variable predicted: body_mass_g
Predictors contrasted: species
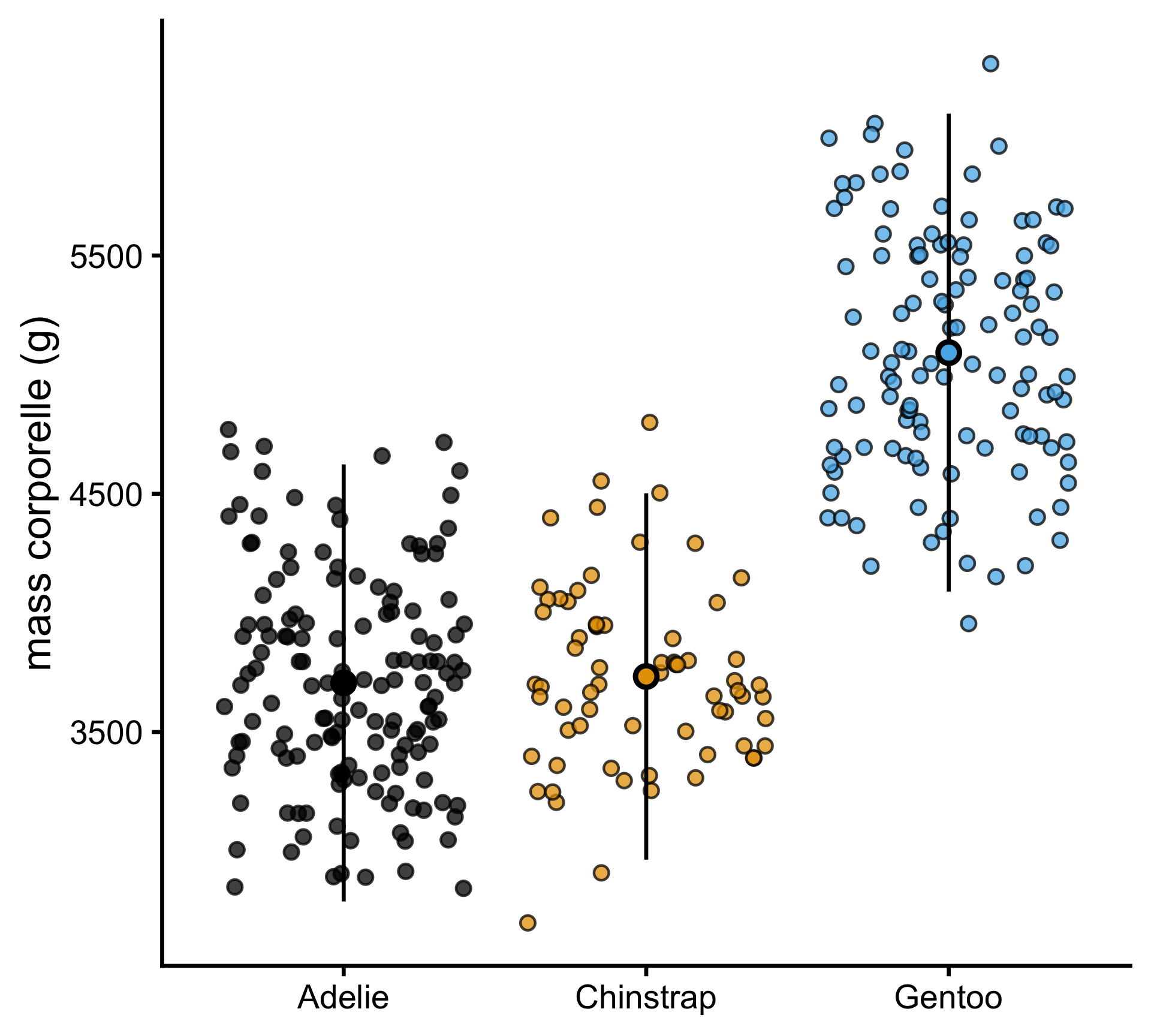
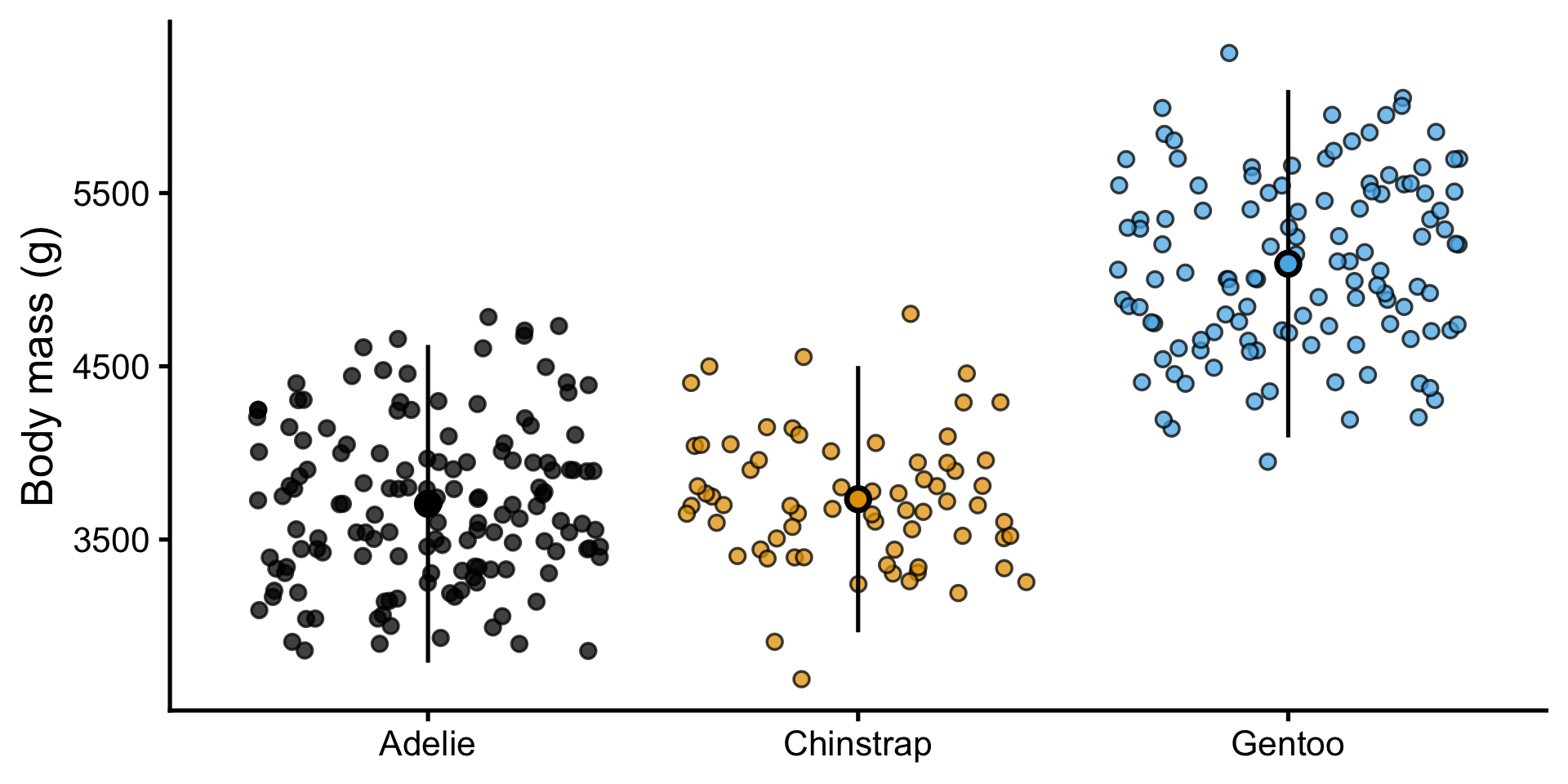
p-value adjustment method: TukeyVisualiser les tests post-hoc
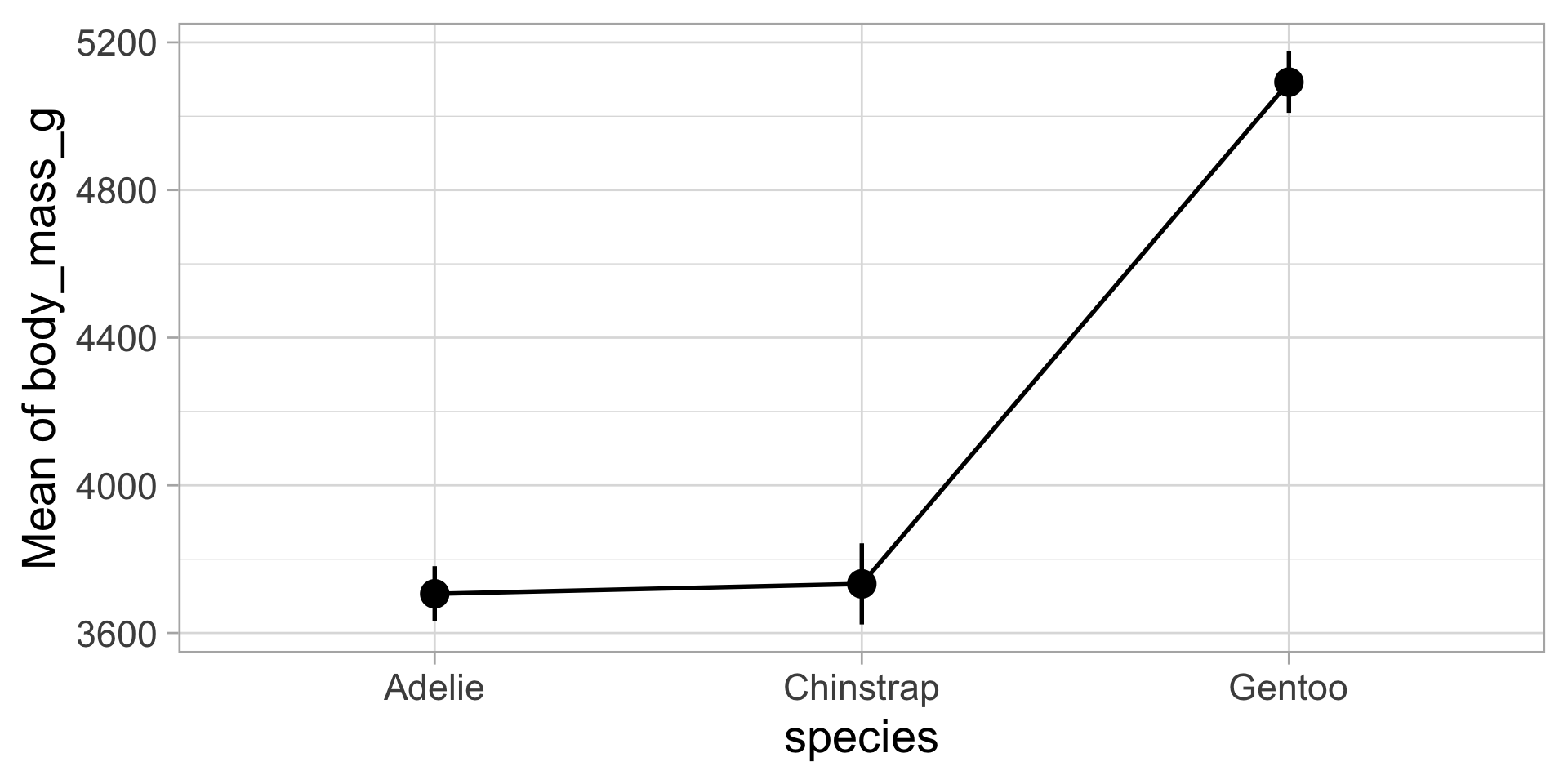
Récemment, les chercheurs s’éloignent des valeurs p comme seuils rigides. L’ampleur de l’effet (importance biologique) importe plus que p < 0,05 !
Recommandation
Tracez l’IC 95%
« Intervalle de confiance à 95% : est une plage calculée de sorte que, si on la répète plusieurs fois, 95% de ces intervalles contiendraient la vraie valeur du paramètre. »
Pas de chevauchement : Les groupes sont statistiquement significativement différents (p < 0,05)
Chevauchement : Peuvent être statistiquement significativement différents, mais l’effet est probablement petit
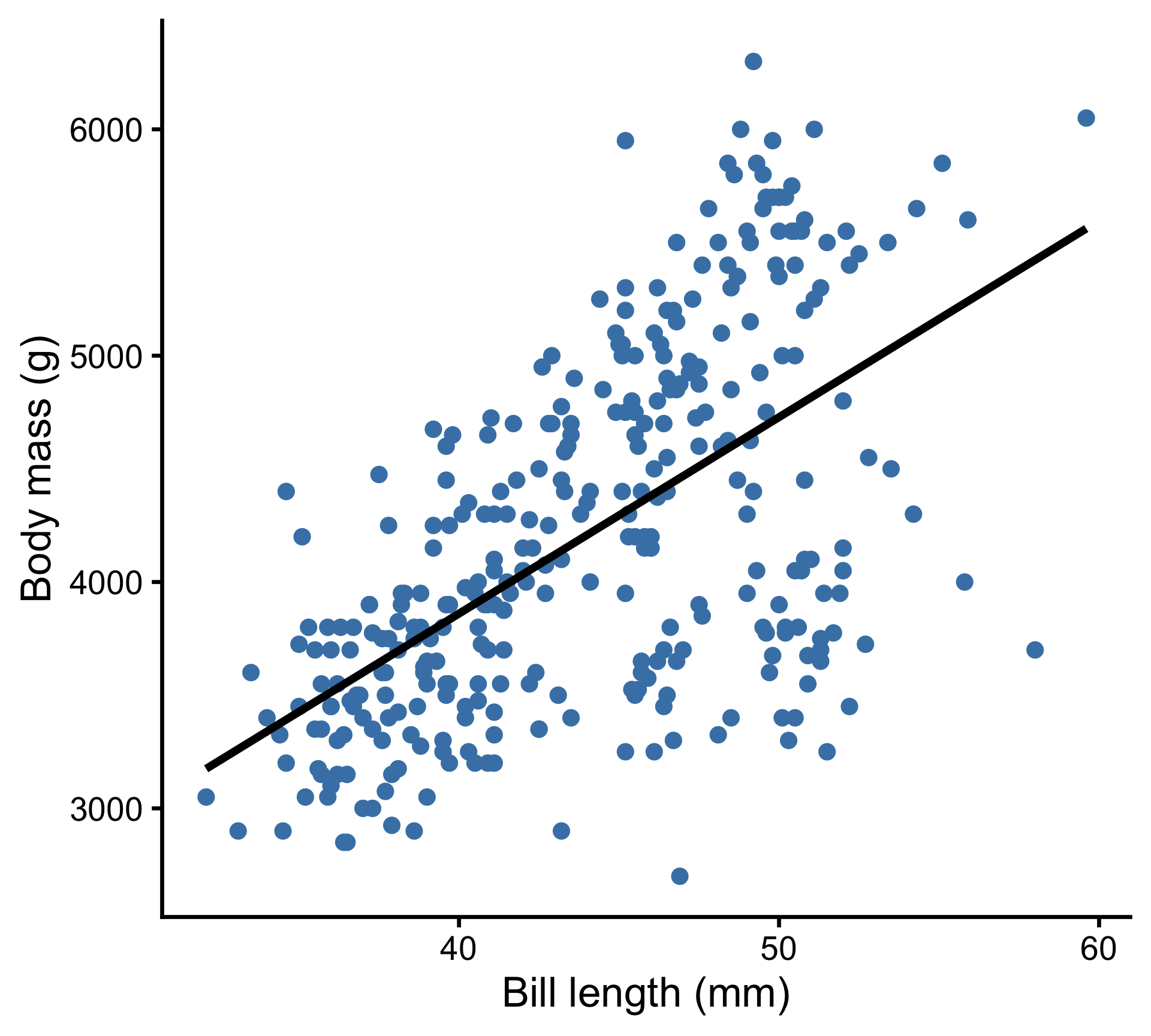
Comparaisons de pentes : ANCOVA
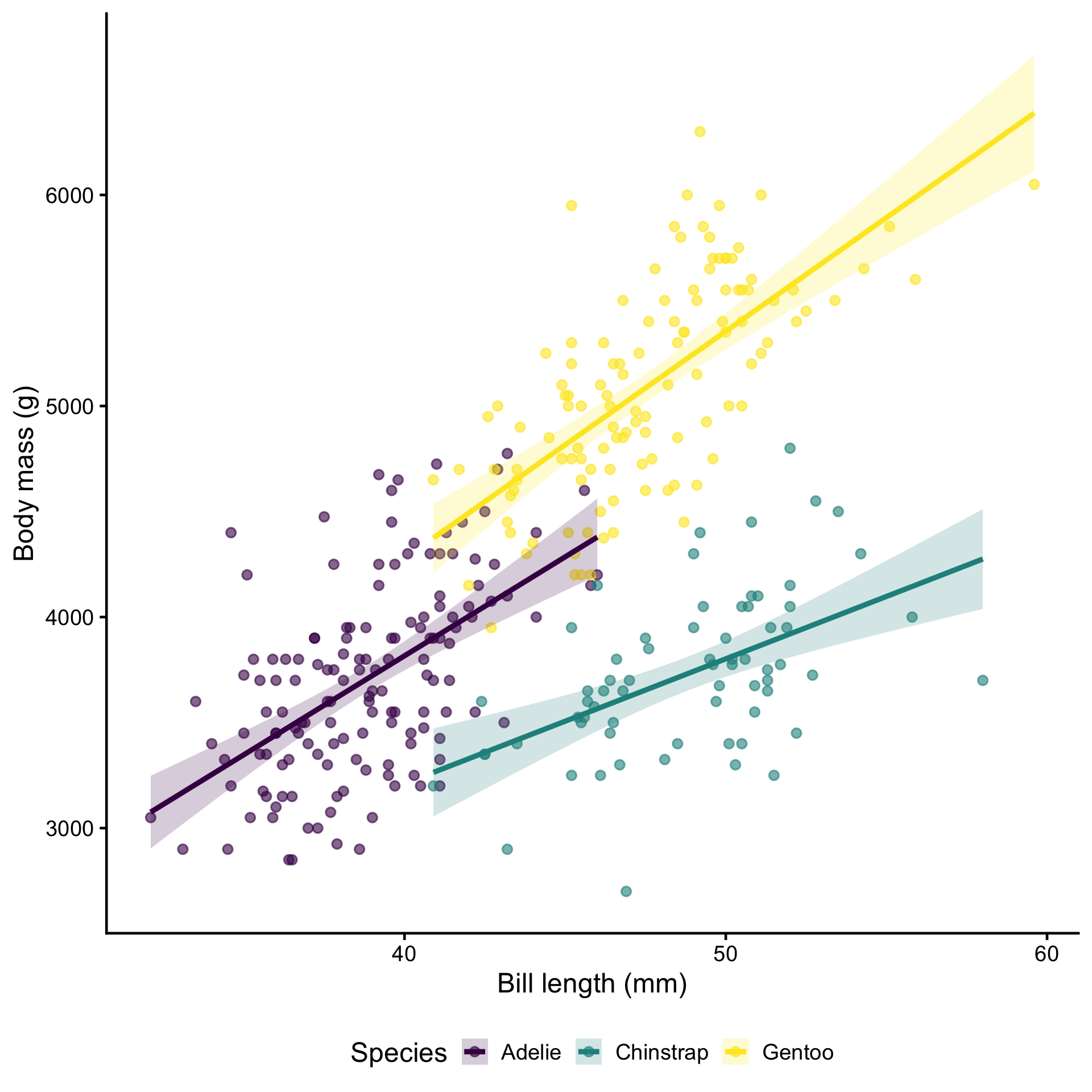
Les pentes diffèrent-elles entre les espèces ?
Analysis of Variance Table
Response: body_mass_g
Df Sum Sq Mean Sq F value Pr(>F)
bill_length_mm 1 74792533 74792533 540.6978 < 2e-16 ***
species 2 94153502 47076751 340.3320 < 2e-16 ***
bill_length_mm:species 2 1081048 540524 3.9076 0.02103 *
Residuals 327 45232583 138326
---
Signif. codes: 0 '***' 0.001 '**' 0.01 '*' 0.05 '.' 0.1 ' ' 1Comparaisons de pentes : ANCOVA
Les pentes diffèrent-elles entre les espèces ?
Marginal Contrasts Analysis
Level1 | Level2 | Difference | SE | 95% CI | t(327) | p
-----------------------------------------------------------------------------
Chinstrap | Adelie | -34.63 | 17.89 | [-69.82, 0.56] | -1.94 | 0.130
Gentoo | Adelie | 13.89 | 16.03 | [-17.64, 45.42] | 0.87 | 0.662
Gentoo | Chinstrap | 48.52 | 17.53 | [ 14.04, 83.01] | 2.77 | 0.016
Variable predicted: body_mass_g
Predictors contrasted: bill_length_mm
Predictors averaged: bill_length_mm (44)
p-value adjustment method: TukeyComparaisons de pentes : ANCOVA
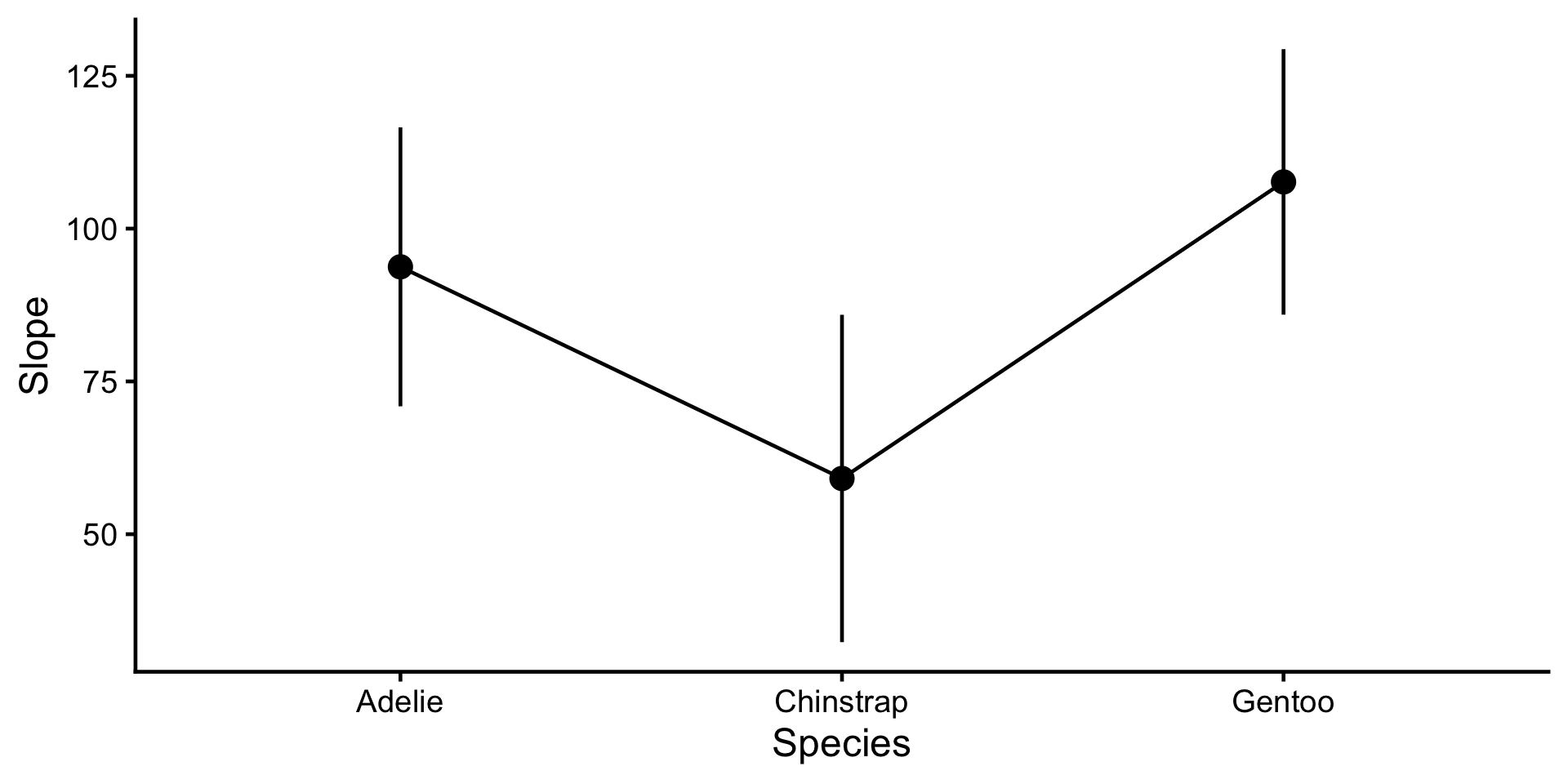
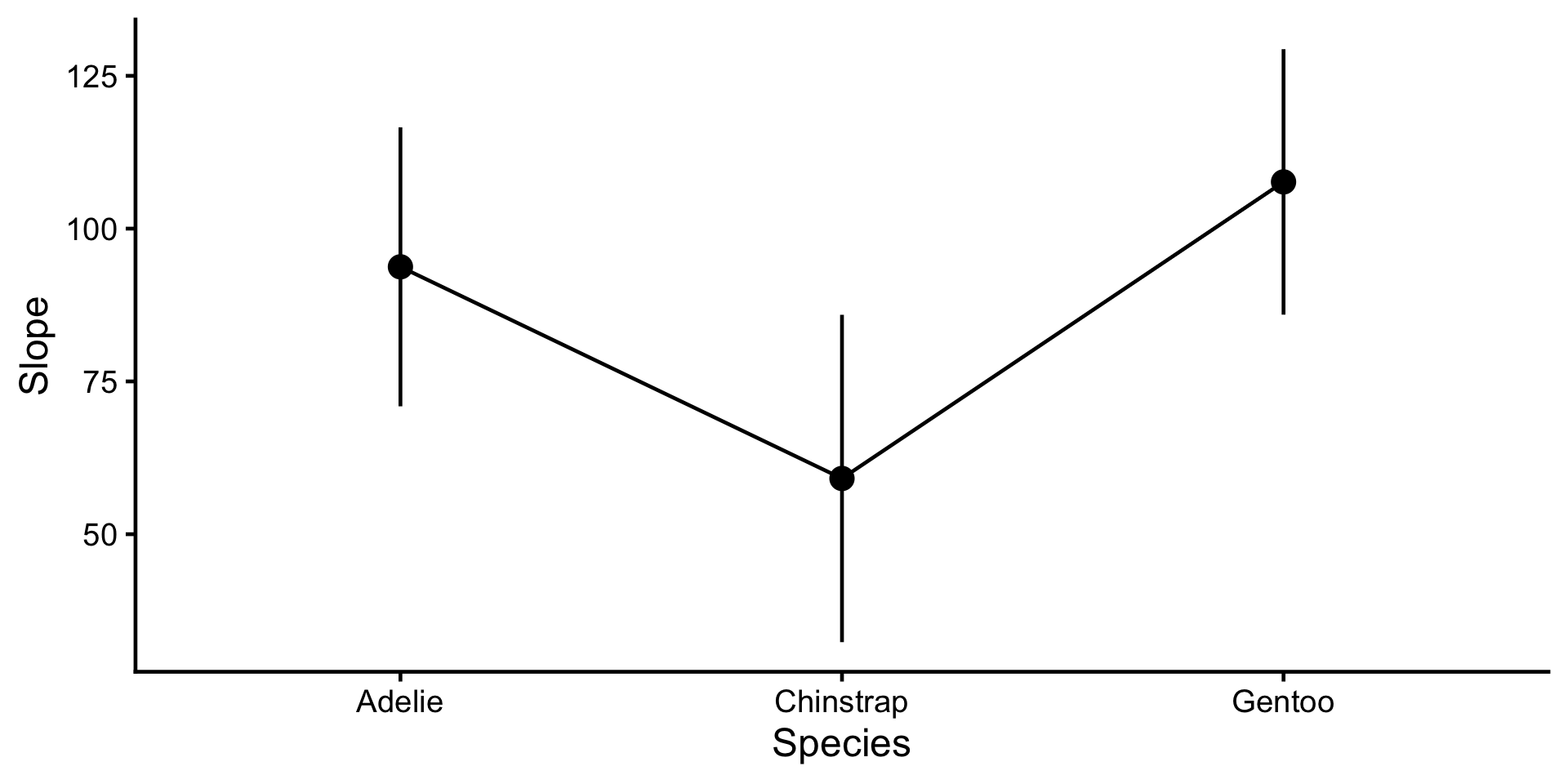
Les pentes diffèrent-elles de 0 ?
Estimated Marginal Effects
species | Slope | SE | 95% CI | t(327) | p
--------------------------------------------------------------
Adelie | 93.75 | 11.60 | [70.92, 116.58] | 8.08 | < .001
Chinstrap | 59.12 | 13.61 | [32.34, 85.90] | 4.34 | < .001
Gentoo | 107.64 | 11.04 | [85.92, 129.36] | 9.75 | < .001
Marginal effects estimated for bill_length_mm
Type of slope was dY/dXÀ vous de jouer
- Allez sur le site du cours
- Allez au calendrier
- Cliquez sur
TP 04 - Connectez-vous à Posit Cloud