ggplot(
data = penguins,
aes(x = bill_length_mm, y = body_mass_g, colour = species)
) +
geom_point() +
labs(x = "Bill length (mm)", y = "Body mass (g)") +
____Indications pour TP 02
Je vous donne ici de l’aide au cas où vous auriez du mal à résoudre les tâches. Veuillez d’abord essayer de résoudre les tâches sans ces indications. Toutes les informations dont vous avez besoin se trouvent dans le document .qmd que je vous ai partagé.
Tâche 1
Utilisez différents thèmes pour le graphique que nous venons de créer ci-dessus. Voici une liste de thèmes standard, mais il existe de nombreux packages R qui élargissent vos choix :
Remplacez la partie ____ par l’un des thèmes de la liste que je vous ai donnée.
Tâche 2
Remplacez le ____ ci-dessous par une échelle de couleur de votre choix.
ggplot(
data = penguins,
aes(x = bill_length_mm, y = body_mass_g, colour = species)
) +
geom_point() +
labs(x = "Bill length (mm)", y = "Body mass (g)") +
___ +
theme_minimal()Remplacez la partie ____ par l’un des exemples d’échelle de couleur que je vous ai donnés, par exemple scale_colour_colourblind() et scale_colour_viridis_d().
Si vous voulez utiliser l’échelle de couleur « entièrement manuelle », vous pouvez l’adapter à quelque chose de plus beau comme : scale_colour_manual(values = c("darkorange", "darkgreen","aquamarine2"))
Tâche 3
Prenez le graphique que nous avons créé ci-dessus. En plus des différentes couleurs, utilisez également différentes formes de points pour les différentes espèces. Remplacez le ____ par le nom de colonne approprié :
ggplot(
data = penguins,
aes(x = bill_length_mm, y = body_mass_g, colour = species, shape = ____)
) +
geom_point() +
labs(x = "Bill length (mm)", y = "Body mass (g)") +
theme_classic()Pensez à comment vous voulez tracer les données. Puisque vous avez déjà utilisé la colonne species pour définir la couleur des points de données, vous pouvez l’utiliser de la même manière pour définir la forme des points de données. Remplacez simplement ____ par species.
Tâche 4
Jusqu’à présent, nous avons utilisé des données catégoriques pour les différentes couleurs. Que se passe-t-il si vous utilisez une variable numérique pour définir les différentes couleurs ? Remplacez le ____ ci-dessous par une colonne numérique, par ex. flipper_length_mm. N’oubliez pas de mettre à jour également les étiquettes utilisées pour la couleur. Changez le ____ dans labs() pour quelque chose d’utile. N’oubliez pas que tout texte doit être enveloppé avec "".
ggplot(
data = penguins,
aes(x = bill_length_mm, y = body_mass_g, colour = ____, shape = species)
) +
geom_point() +
labs(x = "Bill length (mm)", y = "Body mass (g)", colour = ____) +
scale_colour_viridis_c() +
theme_classic()Ci-dessus, vous avez utilisé la colonne species pour les différentes couleurs, maintenant, vous êtes censé utiliser la colonne flipper_length_mm. Comme nom pour la légende (dans labs()), vous pouvez utiliser par exemple "Flipper length (mm)".
Tâche 5
Regardez le graphique que vous venez de créer. Quel est la relation entre la longueur du bec, la masse corporelle et la longueur des nageoires ?
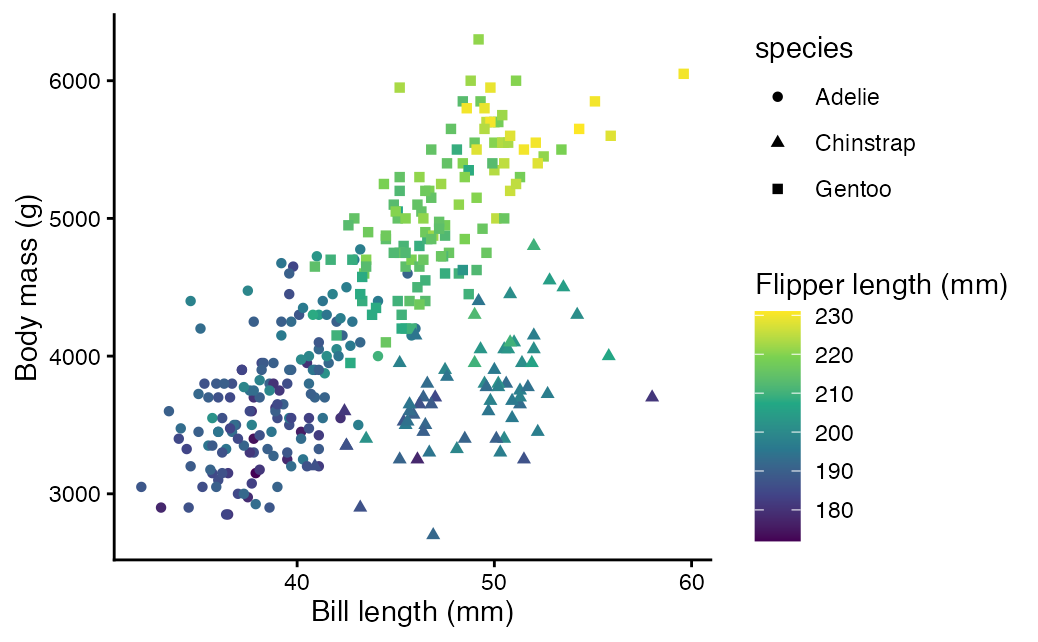
D’abord, regardez uniquement le nuage de points. Essayez de comprendre comment les valeurs d’un axe impactent les valeurs de l’autre axe. Dans l’ensemble, les manchots avec une longueur de bec importante ont-ils aussi une masse corporelle élevée ? Maintenant, essayez d’inclure la longueur des nageoires codée par couleur. Y a-t-il des motifs dans les couleurs des points qui sont liés à l’un ou l’autre axe ? Plus explicitement, la longueur des nageoires augmente-t-elle avec la longueur du bec et/ou la masse corporelle ?
Tâche 6
Vous pouvez modifier la largeur des barres. Cela peut être utile, car chaque barre représente la fréquence d’une plage de valeurs (par exemple, des étapes de 5 mm). Vous pouvez le faire avec l’argument bins. Essayez différentes valeurs ci-dessous et voyez ce qui se passe :
ggplot(data = penguins, aes(x = bill_length_mm)) +
geom_histogram(bins = ____) +
theme_classic()Que se passe-t-il si vous n’utilisez que 1 ou 2 barres ? Que se passe-t-il si vous utilisez 100 ? 500 ? Remplacez le ____ par différentes valeurs et voyez comment le graphique change.
Tâche 7
Maintenant, tracez de la même manière l’île où les manchots ont été observés. Utilisez la colonne island.
ggplot(data = penguins, aes(x = ____)) +
geom_bar(stat = "count") +
theme_classic()Encore une fois, pensez à ce que vous voulez tracer. Vous voulez afficher un graphique en barres avec la fréquence des îles sur l’axe y (calculée automatiquement) et le niveau de l’île (par ex. Torgersen ou Biscoe) sur l’axe x. Par conséquent, vous devez donner island comme l’axe x.
Tâche 8
Dans ce graphique, le point représente la moyenne et la ligne l’écart-type. Faire cela pour les données groupées par île n’est pas très utile. Adaptez le graphique ci-dessous pour qu’il affiche la longueur des nageoires groupée par espèce :
ggplot(data = penguins, aes(x = ____, y = flipper_length_mm)) +
geom_pointrange(stat = "summary", fun.data = mean_sdl) +
theme_classic()Remplacez le ____ par species.
Tâche 9
Que se passe-t-il si vous n’utilisez pas geom_jitter() mais le geom_point() “standard” ? Essayez ci-dessous :
ggplot(data = penguins, aes(x = species, y = flipper_length_mm)) +
____(alpha = .4) +
geom_pointrange(stat = "summary", fun.data = mean_sdl) +
theme_classic()Vous voulez utiliser un “normal” geom_point(). La deuxième ligne sera : geom_point(alpha = .4) +.
Le graphique résultant est-il utile ? Pourquoi ? Comment pourrait-il être amélioré ?
Tâche 10
En dernière étape, essayez de personnaliser le graphique pour que vous réalisiez quelque chose de similaire à celui-ci. Pensez à quelle colonne est utilisée pour quoi.
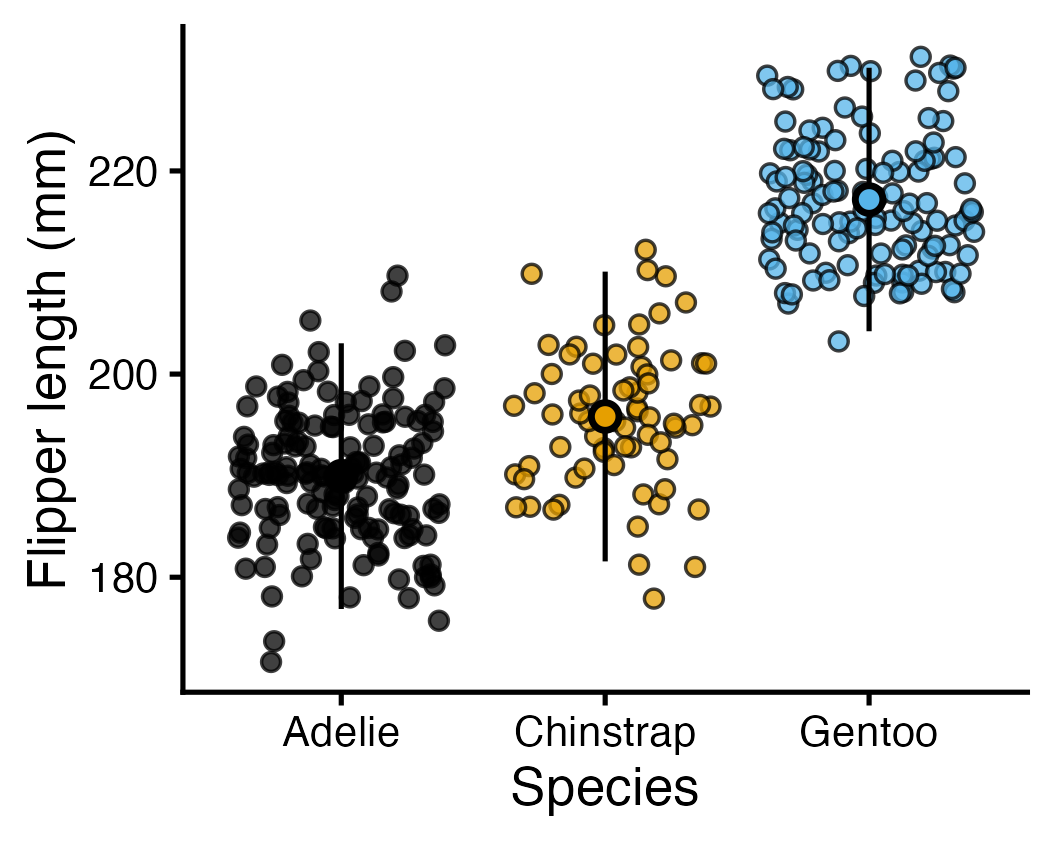
Voici le graphique “base” comme point de départ :
ggplot(data = penguins, aes(x = species, y = flipper_length_mm)) +
geom_jitter(alpha = .4) +
geom_pointrange(stat = "summary", fun.data = mean_sdl) +
theme_classic()Une solution possible est :
ggplot(
data = penguins,
aes(x = species, y = flipper_length_mm, fill = species),
) +
geom_jitter(alpha = .75, shape = 21) +
geom_pointrange(
stat = "summary",
fun.data = mean_sdl,
show.legend = F,
shape = 21
) +
labs(
x = "Species",
y = "Flipper length (mm)"
) +
scale_color_colorblind() +
scale_fill_colorblind() +
theme_classic(base_size = 20) +
theme(legend.position = "none")